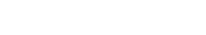チームリーダー
工樂 樹洋
Ph.D.
分子配列比較解析チーム
[2023年3月 終了]
E-mail shigehiro.kuraku[at]riken.jp
[at]を@に変えてください
我々のからだのつくりや生命のいとなみの設計図ともいえるゲノムは、突然創られたものではなく、数十億年にもわたる度重なる変更の産物です。現存のどの生物のゲノムにも歴史があり、その情報を生物種のあいだで比較することによって、過去にどのようなゲノムの改変が起きたのか、推測することができます。ゲノム進化の歴史を紐解くことにより、ヒトをはじめとする多様な生物の現在の活動を支える分子メカニズムの成り立ちを探ることも可能となります。
当研究室では、ゲノム内の多数の遺伝子のあいだの系統関係や進化の時間軸を念頭に置きつつ、先端的なDNA解析技術を駆使して、脊椎動物のゲノム構造やエピゲノム制御メカニズムの進化的変遷について研究を行っています。多様な脊椎動物のゲノムワイドな情報解析を進めながら、そこから得た生物学的知見と技術運用のためのノウハウをヒトや実験動物の広範な生命科学研究につなげることをめざして、分子進化学的・ゲノム学的視野に立った生物多様性リテラシーの普及のための活動も行っています。
研究テーマ
- 分子進化学の手法と生命現象の分子的理解に立脚した生物多様性研究
- 染色体規模のDNA情報取得のための包括的ゲノム解析技術の高度化
- クロマチン構造とその制御を視野に入れた脊椎動物のゲノム進化学
- 大型海棲脊椎動物など重要でありながら情報が乏しい生物の分子情報取得
主要論文
Ohnishi T, Kiyama Y, Arima-Yoshida F, et al.
Cooperation of LIM domain-binding 2 (LDB2) with EGR in the pathogenesis of schizophrenia.
EMBO molecular medicine
13(4), e12574 (2021)
doi: 10.15252/emmm.202012574
Kajikawa E, Horo U, Ide T, et al.
Nodal paralogues underlie distinct mechanisms for visceral left-right asymmetry in reptiles and mammals.
Nature ecology & evolution
4(2), 261-269 (2020)
doi: 10.1038/s41559-019-1072-2
Kadota M, Nishimura O, Miura H, et al.
Multifaceted Hi-C benchmarking: what makes a difference in chromosome-scale genome scaffolding?
GigaScience
9(1), giz158 (2020)
doi: 10.1093/gigascience/giz158
Kishida T, Go Y, Tatsumoto S, et al.
Loss of olfaction in sea snakes provides new perspectives on the aquatic adaptation of amniotes.
Proceedings. Biological sciences
286(1910), 20191828 (2019)
doi: 10.1098/rspb.2019.1828
Hara Y, Takeuchi M, Kageyama Y, et al.
Madagascar ground gecko genome analysis characterizes asymmetric fates of duplicated genes.
BMC Biology
16, 40 (2018)
doi: 10.1186/s12915-018-0509-4
Hara Y, Yamaguchi K, Onimaru K, et al.
Shark genomes provide insights into elasmobranch evolution and the origin of vertebrates.
Nature ecology & evolution
2(11), 1761-1771 (2018)
doi: 10.1038/s41559-018-0673-5
Onimaru K, Kuraku S.
Inference of the ancestral vertebrate phenotype through vestiges of the whole-genome duplications.
Briefings in functional genomics
17(5), 352-361 (2018)
doi: 10.1093/bfgp/ely008
Nishimura O, Hara Y, Kuraku S.
gVolante for standardizing completeness assessment of genome and transcriptome assemblies.
Bioinformatics
33(22), 3635-3637 (2017)
doi: 10.1093/bioinformatics/btx445
Kadota M, Hara Y, Tanaka K, et al.
CTCF binding landscape in jawless fish with reference to Hox cluster evolution.
Scientific Reports
7(1), 4957 (2017)
doi: 10.1038/s41598-017-04506-x
Smith JJ, Kuraku S, Holt C, et al.
Sequencing of the sea lamprey (Petromyzon marinus) genome provide insights into vertebrate evolution.
Nature Genetics
45(4), 415-421 (2013)
doi: 10.1038/ng.2568
Kuraku S.
Impact of asymmetric gene repertoire between cyclostomes and gnathostomes.
Seminars in Cell and Developmental Biology
24(2), 119-127 (2013)
doi: 10.1016/j.semcdb.2012.12.009
Kuraku S, Zmasek CM, Nishimura O, Katoh K.
aLeaves facilitates on-demand exploration of metazoan gene family trees on MAFFT sequence alignment server with enhanced interactivity.
Nucleic acids research
41(Web Server issue), W22-8 (2013)
doi: 10.1093/nar/gkt389
メンバー
門田 満隆
技師
西村 理
技師
種子島 千春
専門技術員
辰見 香織
テクニカルスタッフⅡ
大石 雄太
大学院生リサーチ・アソシエイト
ニュース

2023年5月26日 研究成果
消えるのか?残るのか?

2023年3月28日 研究成果
卵で増えない胎生のサメも卵黄遺伝子を持つ

2023年3月23日 研究成果
ジンベエザメだけに起きた視覚の進化

2022年10月4日 BDRニュース
BDRの研究ネホリハホリ
DNA解析が革新する生物学

2021年6月30日 研究成果
カニクイザルとコモンマーモセットの全ゲノム配列解読に成功

2021年3月19日 BDRニュース
研究者にズームイン
分子配列の謎に迫る
2021年3月3日 研究成果
精神疾患に関与する新しい遺伝子発現調節系の発見
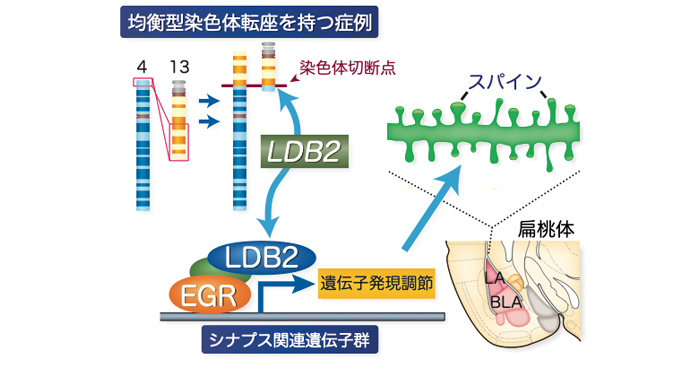
2020年8月21日 BDRニュース
一般向けイベント
中高生のための夏の特別授業「新型コロナウイルスに挑む生命科学・計算科学」を開催

2020年1月9日 研究成果
哺乳類と鳥類の左右非対称性メカニズムの乖離を説明

2019年9月11日 研究成果
ウミヘビ類のゲノム解読に成功
2018年11月28日 研究成果
皮膚で触覚が生まれる仕組みの一端を解明

2018年10月9日 研究成果
サメのゲノムを解読

2018年9月22日 BDRニュース
工樂樹洋UL(分子配列比較解析ユニット)のエッセイが産経新聞の連載「科学の中身」に掲載されました

2018年5月18日 BDRニュース
論文ノート
新しい仲間!ソメワケササクレヤモリ

2018年4月16日 研究成果
爬虫類ソメワケササクレヤモリの全ゲノム解読