チームリーダー
隅山 健太*
Ph.D.
高速ゲノム変異マウス作製研究チーム
[2023年9月 終了]
*現所属名古屋大学大学院生命農学研究科 教授
E-mailksumiyam[at]agr.nagoya-u.ac.jp
[at]を@に変えてください
私たちは初代(G0)マウスでの表現型解析を可能にするため、マウス受精卵への直接ゲノム編集・改変技術(Triple CRISPR法、Tol2トランスジェネシス法)や、新しいマイクロデバイスを用いた簡単確実なアグリゲーション法などの発生工学的技術開発を行っています。また、このゲノム編集技術を応用して哺乳類ゲノムの発現調節メカニズムの解明とその進化に関わるゲノム領域の機能解析も進めています。高次ゲノム構造にも注目し、多種生物間ゲノム配列分子進化解析により抽出した哺乳類獲得形質に関わる配列をゲノム編集技術で機能解析し、哺乳類発生の進化のメカニズムを明らかにしようとしています。 最近の成果として、トリプルCRISPR法の開発があります。従来のゲノム編集マウス作製では、初代のマウスはモザイクとなってしまうため表現型解析が出来ませんでした。私たちはガイドRNAの設計を見直し、一遺伝子内の3箇所を同時にターゲットとすることでほぼ100%標的遺伝子ノックアウトを実現、交配を必要とすることなく初代マウスでの表現型解析を可能にしました。
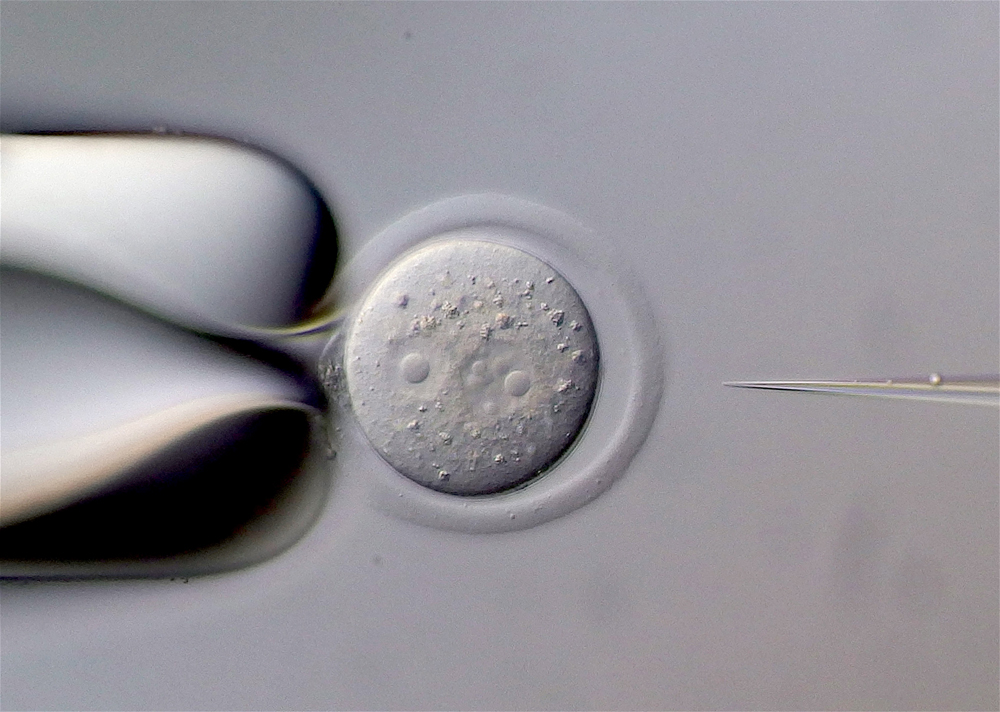
マウス受精卵へのマイクロインジェクション
研究テーマ
- マウス受精卵への高効率直接ゲノム編集技術の開発
- マウス受精卵への新しいトランスジェネシス法の開発
- 哺乳類ゲノムの非コード領域中の遺伝子発現調節機能の解析
- 新奇機能獲得の進化メカニズムの解明
主要論文
Sumiyama K, Matsumoto N, Garçon-Yoshida J, et al.
Easy and efficient production of completely embryonic-stem-cell-derived mice using a micro-aggregation device.
PloS one
13(9), e0203056 (2018)
doi: 10.1371/journal.pone.0203056
Tatsuki F, Sunagawa GA, Shi S, et al.
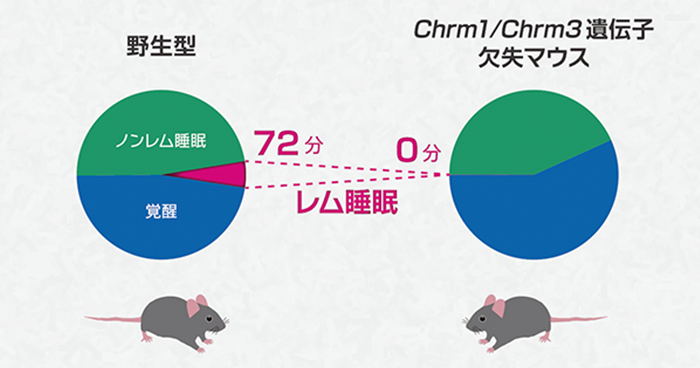
Involvement of Ca2+-Dependent Hyperpolarization in Sleep Duration in Mammals.
Neuron
90(1), 70-85 (2016)
doi: 10.1016/j.neuron.2016.02.032
Sunagawa GA, Sumiyama K, Ukai-Tadenuma M, et al.
Mammalian Reverse Genetics without Crossing Reveals Nr3a as a Short-Sleeper Gene.
Cell Reports
14(3), 662-677 (2016)
doi: 10.1016/j.celrep.2015.12.052
Noguchi M, Sumiyama K, Morimoto M.
Directed Migration of Pulmonary Neuroendocrine Cells toward Airway Branches Organizes the Stereotypic Location of Neuroepithelial Bodies.
Cell Reports
13(12), 2679-2686 (2015)
doi: 10.1016/j.celrep.2015.11.058
Goto A, Nakahara I, Yamaguchi T, et al.
Circuit-dependent striatal PKA and ERK signaling underlies rapid behavioral shift in mating reaction of male mice.
Proceedings Of The National Academy Of Sciences Of The United States Of America
112(21), 6718-6723 (2015)
doi: 10.1073/pnas.1507121112
Amemiya CT, Alfoldi J, Lee AP, et al.
The African coelacanth genome provides insights into tetrapod evolution.
Nature
496(7445), 311-316 (2013)
doi: 10.1038/nature12027
Sumiyama K, Miyake T, Grimwood J, et al.
Theria-Specific Homeodomain and cis-Regulatory Element Evolution of the Dlx3-4 Bigene Cluster in 12 Different Mammalian Species.
Journal of Experimental Zoology Part B-Molecular and Developmental Evolution
318(8), 639-650 (2012)
doi: 10.1002/jez.b.22469
Kamioka Y, Sumiyama K, Mizuno R, et al.
Live Imaging of Protein Kinase Activities in Transgenic Mice Expressing FRET Biosensors.
Cell Structure and Function
37(1), 65-73 (2012)
Sumiyama K, Kawakami K, Yagita K.
A simple and highly efficient transgenesis method in mice with the Tol2 transposon system and cytoplasmic microinjection.
Genomics
95(5), 306-311 (2010)
doi: 10.1016/j.ygeno.2010.02.006
Sumiyama K, Ruddle FH.
Regulation of Dlx3 gene expression in visceral arches by evolutionarily conserved enhancer elements.
Proceedings of the National Academy of Sciences of the United States of America
100(7), 4030-4034 (2003)
doi: 10.1073/pnas.0530119100
Sumiyama K, Irvine SQ, Stock DW, et al.
Genomic structure and functional control of the Dlx3-7 bigene cluster.
Proceedings of the National Academy of Sciences of the United States of America
99(2), 780-785 (2002)
doi: 10.1073/pnas.012584999